如何使用clusterProfiler包利用eggnog-mapper软件注释结果做GO和KEGG富集分析
这篇文章将为大家详细讲解有关如何使用clusterProfiler包利用eggnog-mapper软件注释结果做GO和KEGG富集分析,小编觉得挺实用的,因此分享给大家做个参考,希望大家阅读完这篇文章后可以有所收获。
创新互联公司-专业网站定制、快速模板网站建设、高性价比水城网站开发、企业建站全套包干低至880元,成熟完善的模板库,直接使用。一站式水城网站制作公司更省心,省钱,快速模板网站建设找我们,业务覆盖水城地区。费用合理售后完善,十载实体公司更值得信赖。
第一步是使用eggnog-mapper做功能注释
conda activate emapper
python emapper.py -i orgdb_example/GCF_000002945.1_ASM294v2_protein.faa --output orgdb_example/out -m diamond --cpu 8
将注释结果下载到本地,手动删除前三行带井号的行,第四行开头的井号去掉,文件末尾带井号的行去掉。
利用R语言将注释结果整理成enricher函数需要的输入格式
library(stringr)
library(dplyr)
egg<-read.table("out.emapper.annotations",sep="\t",header=T)
egg[egg==""]<-NA
gterms <- egg %>%
select(query_name, GOs) %>%
na.omit()
gene2go <- data.frame(term = character(),
gene = character())
for (row in 1:nrow(gterms)) {
gene_terms <- str_split(gterms[row,"GOs"], ",", simplify = FALSE)[[1]]
gene_id <- gterms[row, "query_name"][[1]]
tmp <- data_frame(gene = rep(gene_id, length(gene_terms)),
term = gene_terms)
gene2go <- rbind(gene2go, tmp)
}
head(gene2go)
> head(gene2go)
# A tibble: 6 x 2
gene term
<chr> <chr>
1 NP_001018179.1 GO:0003674
2 NP_001018179.1 GO:0003824
3 NP_001018179.1 GO:0004418
4 NP_001018179.1 GO:0005575
5 NP_001018179.1 GO:0005622
6 NP_001018179.1 GO:0005623
获得一个两列的数据框,有了这个数据框就可以做GO富集分析了
在 https://www.jianshu.com/p/9c9e97167377 这篇文章里的评论区有人提到上面用到的for循环代码效率比较低,他提供的代码是
gene_ids <- egg$query_name
eggnog_lines_with_go <- egg$GOs!= ""
eggnog_lines_with_go
eggnog_annoations_go <- str_split(egg[eggnog_lines_with_go,]$GOs, ",")
gene_to_go <- data.frame(gene = rep(gene_ids[eggnog_lines_with_go],
times = sapply(eggnog_annoations_go, length)),
term = unlist(eggnog_annoations_go))
head(gene_to_go)
> head(gene_to_go)
gene term
1 NP_001018179.1 GO:0003674
2 NP_001018179.1 GO:0003824
3 NP_001018179.1 GO:0004418
4 NP_001018179.1 GO:0005575
5 NP_001018179.1 GO:0005622
6 NP_001018179.1 GO:0005623
用这个代码替换for循环,确实快好多。
首先准备一个基因列表,我这里选取gene2go中的前40个基因作为测试 还需要为TERM2GENE=参数准备一个数据框,第一列是term,第二列是基因ID,只需要把gene2go的列调换顺序就可以了。
library(clusterProfiler)
gene_list<-gene2go$gene[1:40]
term2gene<-gene2go[,c(2,1)]
df<-enricher(gene=gene_list,
pvalueCutoff = 0.05,
pAdjustMethod = "BH",
TERM2GENE = term2gene)
head(df)
barplot(df)
dotplot(df)
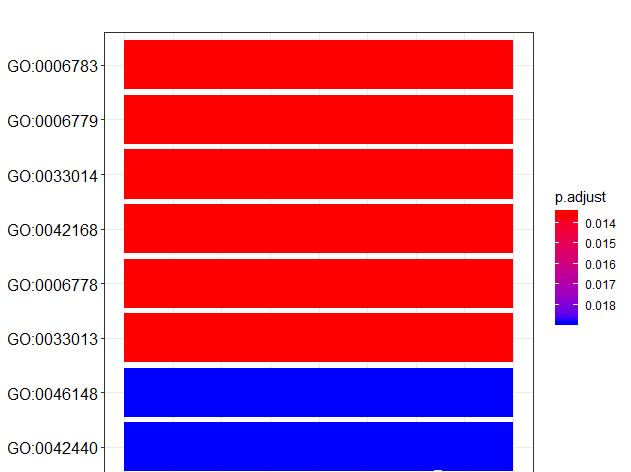
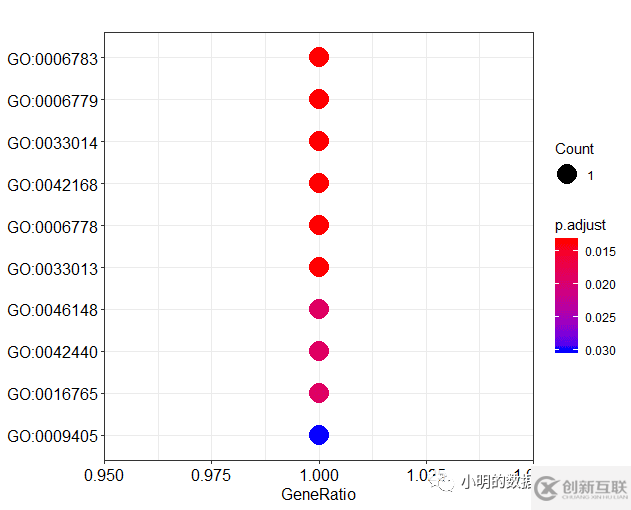
y轴的标签通常是GO term (就是文字的那个)而不是GO id。clusterProfiler包同样提供了函数对ID和term互相转换。go2term()go2ont()
df<-as.data.frame(df)
head(df)
dim(df)
df1<-go2term(df$ID)
dim(df1)
head(df1)
df$term<-df1$Term
df2<-go2ont(df$ID)
dim(df2)
head(df2)
df$Ont<-df2$Ontology
head(df)
df3<-df%>%
select(c("term","Ont","pvalue"))
head(df3)
library(ggplot2)
ggplot(df3,aes(x=term,y=-log10(pvalue)))+
geom_col(aes(fill=Ont))+
coord_flip()+labs(x="")+
theme_bw()
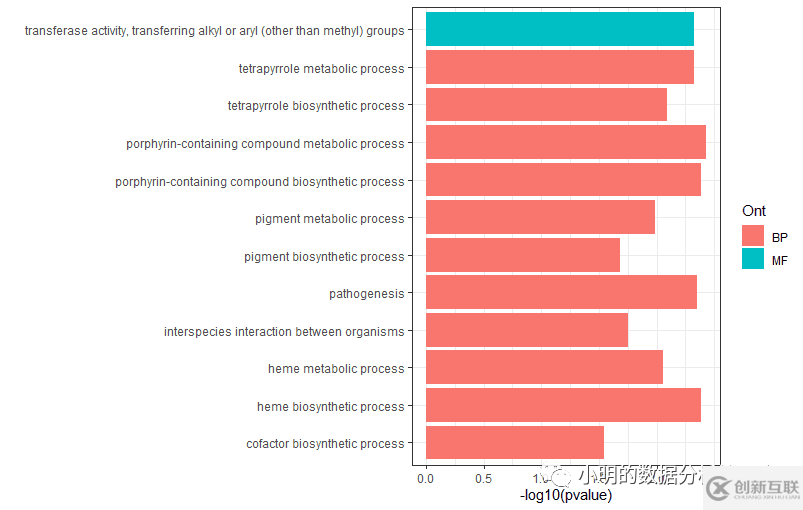
这里遇到一个问题:数据框如何分组排序?目前想到一个比较麻烦的办法是将每组数据弄成一个单独的数据框,排好序后再合并。
library(stringr)
library(dplyr)
library(clusterProfiler)
egg<-read.table("out.emapper.annotations",sep="\t",header=T)
egg[egg==""]<-NA
gene2ko <- egg %>%
dplyr::select(GID = query_name, Ko = KEGG_ko) %>%
na.omit()
head(gene2ko)
head(gene2go)
gene2ko[,2]<-gsub("ko:","",gene2ko[,2])
head(gene2ko)
#kegg_info.RData这个文件里有pathway2name这个对象
load(file = "kegg_info.RData")
pathway2gene <- gene2ko %>% left_join(ko2pathway, by = "Ko") %>%
dplyr::select(pathway=Pathway,gene=GID) %>%
na.omit()
head(pathway2gene)
pathway2name
df<-enricher(gene=gene_list,
pvalueCutoff = 0.05,
pAdjustMethod = "BH",
TERM2GENE = pathway2gene,
TERM2NAME = pathway2name)
dotplot(df)
barplot(df)
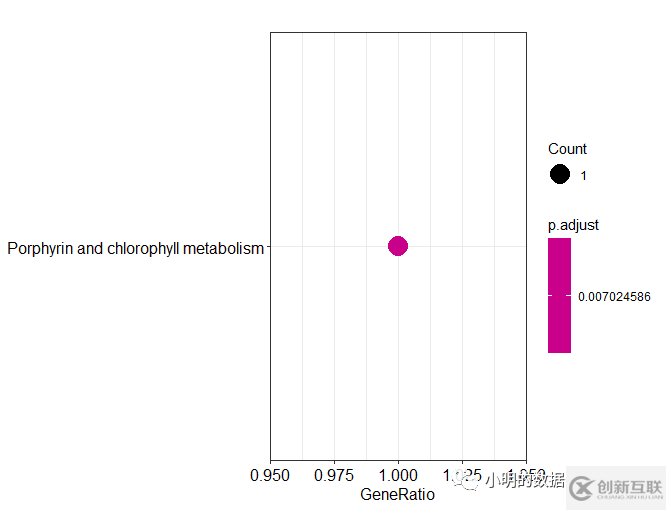
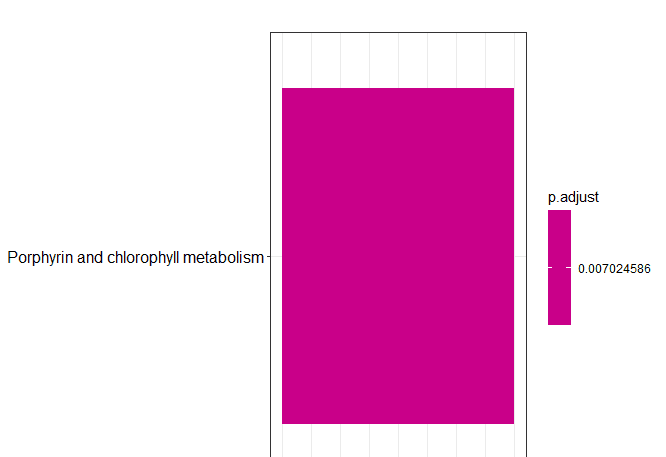
以上最开始的输入文件是eggnog-mapper软件本地版注释结果,如果用在线版获得的注释结果,下载的结果好像没有表头,需要自己对应好要选择的列。
关于“如何使用clusterProfiler包利用eggnog-mapper软件注释结果做GO和KEGG富集分析”这篇文章就分享到这里了,希望以上内容可以对大家有一定的帮助,使各位可以学到更多知识,如果觉得文章不错,请把它分享出去让更多的人看到。
网站标题:如何使用clusterProfiler包利用eggnog-mapper软件注释结果做GO和KEGG富集分析
本文路径:https://www.cdcxhl.com/article4/jiesoe.html
成都网站建设公司_创新互联,为您提供自适应网站、网站内链、企业网站制作、标签优化、微信公众号、网站策划
声明:本网站发布的内容(图片、视频和文字)以用户投稿、用户转载内容为主,如果涉及侵权请尽快告知,我们将会在第一时间删除。文章观点不代表本网站立场,如需处理请联系客服。电话:028-86922220;邮箱:631063699@qq.com。内容未经允许不得转载,或转载时需注明来源: 创新互联
- Google Fonts 网页设计师必用 2019-09-30
- 成都外贸推广:充分利用新Google Search Console的7个步骤 2016-03-01
- 为什么你的Google推广效果不佳? 2016-03-10
- Google推广主要有两种操作方式:1、竞价广告,2、优化(SEO) 2016-04-17
- Google积极的鼓励网站设计公司使用新的网页设计技术。 2019-09-26
- Google成功之谜 2016-05-18
- 讲述一下google和百度优化之间的差异化 2016-01-23
- Google优化推广的重要性,品牌大于品质! 2016-03-08
- Google最新收录规则,怎样才能让网站快速被Google收录 2015-02-07
- 什么是Google Ads推广(谷歌推广)?需要做吗? 2023-05-05
- google搜索引擎优化什么时间做效果最好? 2015-01-12
- 优化您的Google我的商家信息,进行本地推广 2016-02-29